Ansa Tecnologia
Venerdì 20 Marzo 2026
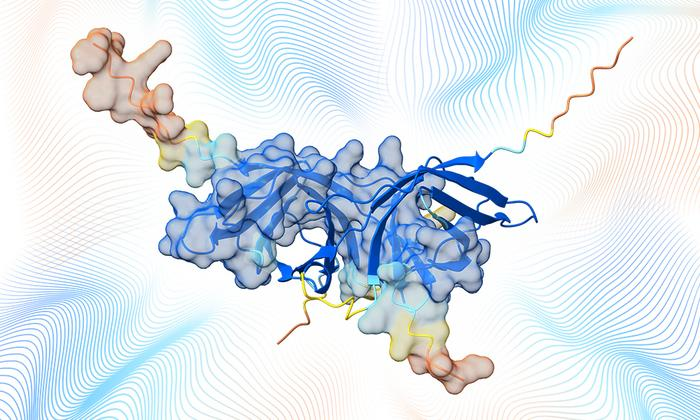
Il database AlphaFold si amplia per capire meglio biologia umana
Le strutture molecolari di milioni di complessi proteici sono state aggiunte al grande database pubblico di AlphaFold , il sistema di intelligenza artificiale sviluppato da Google DeepMind per prevedere la struttura delle proteine. Questo ampio aggiornamento, focalizzato sulle molecole più rilevanti per la biologia umana e le malattie (compresi i batteri considerati prioritari dall'Organizzazione mondiale della sanità), punta ad accelerare la ricerca scientifica contribuendo ad affrontare le grandi sfide sanitarie a livello globale. Il risultato è frutto di una collaborazione internazionale con l'Istituto europeo di bioinformatica del Laboratorio europeo di biologia molecolare (Embl-Ebi), Nvidia e l'Università nazionale di Seul in Corea del Sud.
Questo è il primo passo di un ambizioso progetto che mira ad aggiungere un'ampia gamma di previsioni sulla struttura dei complessi proteici al database AlphaFold. La collaborazione ha già calcolato previsioni per 30 milioni di complessi. Di questi, 1,7 milioni di previsioni di omodimeri (ovvero complessi proteici formati da due proteine identiche) ad alta affidabilità sono state aggiunte al database . Altri 18 milioni sono omodimeri a minore affidabilità , disponibili in un elenco e per il download in blocco. I restanti sono eterodimeri (ovvero complessi proteici formati da subunità diverse), attualmente in fase di analisi e valutazione . Nei prossimi mesi verranno calcolate ulteriori previsioni di complessi proteici e verranno aggiunte al database AlphaFold previsioni ad alta affidabilità. Il lavoro è descritto in modo più dettagliato in un articolo non ancora sottoposto a revisione fra pari (preprint).
© RIPRODUZIONE RISERVATA









